Kompaktlexikon der Biologie: Desoxyribonucleinsäure
Desoxyribonucleinsäure, Abk.: DNA, DNS, ein langes Polymer, das i.d.R. aus den vier Nucleotiden Adenosinmonophosphat, Cytidinmonophosphat, Guanosinmonophosphat und Thymidinmonophosphat als Grundbausteinen besteht, und, von RNA-Viren und RNA-Bakteriophagen abgesehen, in allen Zellen als Träger der genetischen Information fungiert. Dort kommt die DNA überwiegend in den Chromosomen (Chromatin, Eucyte) oder chromosomenähnlichen Strukturen der Protocyte (Bakterienchromosom) vor. Jedes Chromatid eines Chromosoms besteht aus einem DNA-Doppelstrang. Extrachromosomal ist DNA in den Mitochondrien (Chondrom) und Plastiden (Plastom) bzw. als Plasmide vorhanden. Was die Größe einzelner DNA-Moleküle anbelangt, unterscheiden sich die mehrere Tausend Basenpaare großen Plasmide, Phagen-DNAs und Genome der Organellen von den aus vielen Millionen Basenpaaren bestehenden DNA-Strängen eukaryotischer Organismen ( vgl. Tab. ). Die DNA liegt fast immer doppelsträngig als Doppelhelix vor, bei der die beiden DNA-Stränge antiparallel zueinander verlaufen. Lediglich eine Reihe von Bakteriophagen und Viren besteht aus einzelsträngiger DNA.
Die DNA ist zur identischen Reduplikation fähig (Replikation) und die in ihr enthaltene Erbinformation wird während der Transkription in die eng verwandten Ribonucleinsäuren umgeschrieben, die in der Zelle vielfältige Aufgaben übernehmen (Ribosomen Translation).
Chemisch gesehen handelt es sich bei der DNA um ein Polynucleotid, in dem die einzelnen Nucleotide über Phosphodiesterbrücken miteinander verbunden sind, wobei die α-Phosphatgruppe am 5'-Kohlenstoff eines Nucleotids mit dem 3'-Kohlenstoff eines anderen Nucleotids verestert ist (DNA-Polymerasen, Nucleinsäuren). Dadurch erhalten DNA-Moleküle zwei unterschiedliche Enden und somit eine Orientierung, nämlich ein so genanntes 5'-Ende (5'-P-Terminus), dessen Triphosphatgruppe nicht an einer Esterbindung beteiligt ist, und am anderen Ende das so genannte 3'-Ende (3'-OH-Terminus) mit einer freien Hydroxylgruppe. Zahlreiche Enzyme sind in der Lage, die Ausbildung der Phosophodiesterbindung zu katalysieren (z.B. DNA-Poylmerasen, DNA-Ligase) bzw. hydrolytisch zu spalten (z.B. Desoxyribonuclease, DNA-Topoisomerase). Ferner bedienen sich sowohl prokaryotische als auch eukaryotische Zellen einer Reihe unterschiedlicher Mechanismen, um chemische oder biophysikalische Schäden der DNA zu beheben (DNA-Reparatur, Mutation).
Unter physiologischen Bedingungen ist die DNA nicht als Säure, sondern als so genanntes Polyanion vorhanden und interagiert zur Aufrechterhaltung der Elektroneutralität mit Ionen (z.B. K+, NH4+), Aminen und basischen Proteinen (Histone).Neben den bereits genannten n cleotiden enthalten DNAs einiger Viren andere Basen, wie z.B. 5-Hydroxylmethyluracil anstatt Thymin. Außerdem können sie unterschiedlich stark methyliert sein (DNA-Methylierung).
Die ursprünglich durch J. Watson und F. Crick beschriebene Doppelhelix wird inzwischen als so genannte B-Form bezeichnet und unterscheidet sich von weiteren Formen (A-Form, Z-DNA, P-Form) in der Anzahl der Basenpaare pro Windung, dem helikalen Durchmesser und darin, ob sie rechts- oder linksgedreht sind ( vgl. Abb. ). Inwieweit diese durch die Wahl der physikalischen Bedingungen wie Wassergehalt, Vorhandensein bestimmter Ionen oder eine hohe Ionenstärke entstehenden Formen in vivo vorkommen, ist unklar. So kommt die linksgängige Z-DNA (benannt nach den im Zickzack verlaufenden Phosphatgruppen) auch innerhalb der B-Form vor; sie könnte an der Genregulation beteiligt sein oder die im Verlauf der Transkription von der RNA-Polymerase erzeugte negative Torsionsspannung stabilisieren. Torsionsspannungen treten in allen DNA-Molekülen auf, die wie virale, bakterielle und eukaryotische DNA keine freien Enden aufweisen, da sie als ringförmige Moleküle oder aber in Chromosomen organisiert sind. Dadurch kann die DNA nicht mehr frei im Raum drehen, wodurch es zu einer Superspiralisierung (supercoil) kommt. Für die Auflösung dieser Strukturen sind die DNA-Topoisomerasen und DNA-Helicasen verantwortlich.
Dass die in den Chromosomen enthaltene DNA der Träger der Erbinformation ist, war während der ersten Hälfte des 20. Jh. noch nicht akzeptiert, da ein aus lediglich vier Bausteinen bestehendes Molekül nicht geeignet schien, die genetische Vielfalt erklären zu können. So war man der Ansicht, dass Gene aus Proteinen bestehen, die eine große Variabilität bieten. Als in den 1930er- und 1940er-Jahren das so genannte transformierende Prinzip genauer untersucht wurde, das bei Streptococcus pneumoniae für die Umwandlung von avirulenten in virulente Stämme verantwortlich ist, stellte sich heraus, dass tatsächlich DNA genetische Information erhält. 1944 gelang O.T. Avery und seinen Mitarbeitern der experimentelle Beweis, dass es sich bei dem transformierenden Prinzip um DNA handelt und 1952 kamen A. Hershey und Martha Chase mit Hilfe von Radioisotopenmarkierungen am T2-Phagen von Escherichia coli zu dem Schluss, dass die genetische Information für die Hüllproteine des Phagen in dessen DNA enthalten ist. Damit war eindeutig bewiesen, dass DNA und nicht Protein als genetisches Material fungieren.
Zur Untersuchung der DNA stehen heute zahlreiche Verfahren zur Verfügung, mit denen z.B. bestimmte DNA-Abschnitte vervielfältigt (DNA-Klonierung, Polymerasekettenreaktion), der Größe nach aufgetrennt (Elektrophorese) oder aber in ihrer Sequenz analysiert (DNA-Sequenzierung) werden können. Viele Enzyme, die an Replikation und Transkription beteiligt sind, können hierzu auch in vitro eingesetzt werden (Restriktionsenzyme, Desoxyribonucleasen).

Desoxyribonucleinsäure: Modell eines doppelsträngigen DNA-Moleküls. Links ein vereinfachtes Modell, das einen Ausschnitt von 19 Basenpaaren zeigt und dem ursprünglichen Watson-Crick-Modell der Doppelhelix ähnelt. Z = Zucker (2-Desoxyribose), P = Phosphorsäure, A = Adenin, C = Cytosin, G = Guanin, T = Thymin. Rechts ein Kalottenmodell der DNA, das außen das „Zucker-Phosphat-Rückgrat“ und innen die Basenpaare sowie die große und kleine Furche der Doppelhelix erkennen lässt
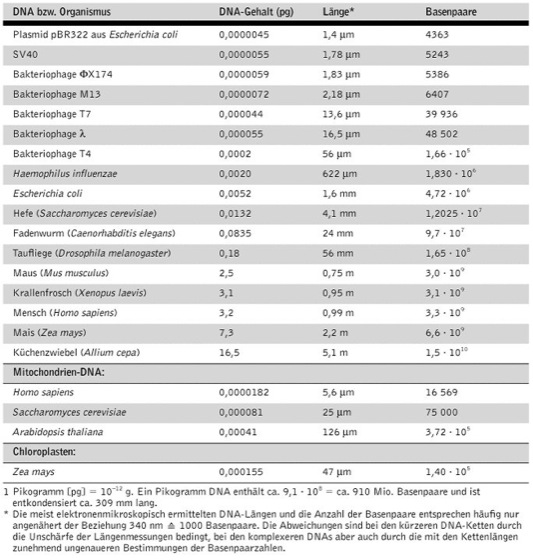
Desoxyribonucleinsäure: Größen von DNS bzw. Größe des haploiden Genoms ausgewählter Organismen (sortiert nach DNA-Gehalt)
Schreiben Sie uns!