Lexikon der Biochemie: Proteinbiosynthese
Proteinbiosynthese, Translation, ein zyklischer, energieverbrauchender Mehrschrittprozess, in dem freie Aminosäuren der Zellen zu Polypeptiden mit genetisch determinierter Sequenz polymerisiert werden. Bei der P. geschieht die Übersetzung der genetischen Information, die in der Nucleotidsequenz der mRNA gespeichert ist, in die Aminosäuresequenz des Proteins. An der P. sind messenger-RNA, Ribosomen, transfer-RNA, Aminosäuren sowie eine Reihe von Enzymen und Proteinfaktoren beteiligt, die meist mehr oder weniger fest integrierte Bestandteile der Ribosomen sind. Außerdem sind als niedermolekulare Cofaktoren Kationen und als Energielieferanten ATP und GTP notwendig. Der Vorgang läuft bei Prokaryonten und Eukaryonten ihn ähnlicher Weise ab, wenngleich letztere mehr Faktoren einbeziehen. Es existiert eine standardisierte Nomenklatur für die "Faktoren", die an der Initiation (IF-1, IF-2, usw.), Elongation (EF-1, usw.) und Termination (release factor, RF) beteiligt sind. Zur Unterscheidung von prokaryontischen Faktoren, wird eukaryontischen Faktoren ein "e" vorgestellt (eIF-1 usw., Tab.).
Man unterscheidet vier Phasen der P.:
1) Die Aktivierung der Aminosäuren und deren Übertragung auf spezifische tRNA (Aminoacyl-tRNA-Synthetasen). Diese Phase ist nicht an die Gegenwart der Polysomen gebunden; die drei folgenden Phasen der P. laufen nacheinander an jedem Ribosom der Polysomen ab.
2)Die Initiation (Einleitungsphase) muss mit einer kleinen Ribosomenuntereinheit starten; 80S- bzw. 70S-Ribosomen sind inaktiv und unter physiologischen Bedingungen verläuft ihre Dissoziation in Untereinheiten sehr langsam. In E. coli wird die Dissoziation der Ribosomen durch den Faktor IF-1 gefördert. Das Protein IF-3 (bzw. eIF-3) verhindert die Assoziation der Untereinheiten, wodurch die kleine Untereinheit für die Initiation zur Verfügung steht. In Eukaryonten besteht der erste Schritt in der Bindung der Initiator-tRNA (Met-tRNAf) zusammen mit eIF-2 und GTP an die 40S-Untereinheit. In Eukaryonten kann dies entweder den ersten Schritt darstellen oder den zweiten, der nach der mRNA-Bindung folgt. Der zusammengesetzte prokaryontische Komplex aus 30S-Untereinheit, IF-1, -2 und -3, sowie GTP und mRNA mit fMet-tRNAf heißt 30S-Initiationskomplex. Der entsprechende Initiationskomplex in Eukaryonten enthält als weitere Faktoren eIF-4 (besteht aus mehreren Proteinen) und ATP, die für die Bindung der mRNA benötigt werden, setzt sich also wie folgt zusammen: 40S : eIF-3 : Met-tRNAf : eIF-2 : GTP : eIF-4 : mRNA.
Sowohl für Prokaryonten als auch für Eukaryonten ist das Initiationscodon auf der mRNA AUG, der Mechanismus, nach dem das Ribosom es ausfindig macht, ist jedoch unterschiedlich. Prokaryontische Ribosomen erkennen anscheinend Sequenzen der mRNA upstream (in Richtung 5'-Ende) vom AUG-Codon. Diese Sequenzen sind zu einem Teil des 16S-rRNA-Moleküls komplementär. Die 70S-Ribosomen können entweder am ersten AUG in der mRNA beginnen oder an einem internen AUG und können sogar zirkuläre mRNA translatieren. Eukaryontische Ribosomen müssen dagegen mit dem AUG starten, das dem 5'-Ende des Messengers am nächsten liegt. Die m7G5'pppX-"Cap" (messenger-RNA) scheint das System zu leiten, jedoch gibt es auch eukaryontische mRNA ohne Cap, die ebenfalls translatiert werden können. Vermutlich muss das Ribosom an der mRNA entlang in downstream-Richtung "wandern", bis es an das erste AUG gelangt. Wahrscheinlich stellt ATP die Energie für diesen Vorgang zur Verfügung.
In Prokaryonten und Eukaryonten wird der Initiationskomplex durch Abspaltung des Initiationsfaktors 3 auf die Addition der großen ribosomalen Untereinheit vorbereitet. In Bakterien scheint die 50S-Untereinheit einfach den IF-3 zu ersetzen, während IF-1 und IF-2 anschließend den Komplex verlassen. In Eukaryonten katalysiert ein weiterer Faktor, der eIF-5, die Abspaltung der vorhergehenden Initiationsfaktoren und die Bindung der 60S-Untereinheit. In beiden Fällen ist an der Freisetzung des Initiationsfaktors 2 die Hydrolyse des gebundenen GTP beteiligt. Die Met-tRNAf ist an der P-Bindungsstelle der großen ribosomalen Untereinheit gebunden.
3) Elongation (Verlängerungsphase, Abb.). Das Ribosom kann zwei tRNA-Moleküle gleichzeitig aufnehmen. An einer Stelle, der P-Bindungsstelle, trägt das Ribosom den Met-tRNA- bzw. den Peptid-tRNA-Komplex; die andere (A-Bindungsstelle) nimmt die Aminoacyl-tRNA auf. An diese wird ein Komplex aus GTP, Elongationsfaktor TU und Aminoacyl-tRNA gebunden. Die tRNA muss dem nächsten Codon, das abgelesen wird, entsprechen; der Elongationsfaktor ist vermutlich dafür mitverantwortlich, die tRNA genau zum richtigen Nucleotidtriplett zu führen. Das GTP wird dann zu GDP hydrolysiert und der EF-TU : GDP-Komplex verlässt das Ribosom. Das GDP wird vom Faktor abgespalten, wenn dieser mit dem Elongationsfaktor TS einen Komplex bildet: EF-TU : EF-TS. Der EF-TU besitzt eine höhere Affinität zu GDP als zu GTP, während der Komplex mit EF-TS eine höhere Affinität für GTP hat, welches den EF-TS verdrängt. Der EF-TU-GTP-Komplex ist bereit, ein anderes Aminoacyl-tRNA-Molekül aufzunehmen und den Zyklus erneut zu durchlaufen. Das Ribosom katalysiert eine Reaktion zwischen der Carboxylgruppe des Besetzers auf der P-Bindungsstelle und der (freien) Aminogruppe des Besetzers auf der A-Seite. Die Peptidyl-Transferase-Aktivität, die diese Reaktion katalysiert, ist dem Ribosom intrinsisch.
Der letzte Schritt der Elongation stellt das Fortschreiten des Ribosoms relativ zur mRNA dar, das von der Translokation der Peptidyl-tRNA von der A- zur P-Bindungsstelle begleitet ist. An diesem Schritt ist der Elongationsfaktor G beteiligt; bei Abwesenheit dieses Faktors findet die Translokation mit langsamer Geschwindigkeit statt. An das Ribosom bindet sich ein Komplex aus EF-G und GTP. Im Verlauf der Reaktion wird GTP hydrolysiert. Gleichzeitig wird die deacylierte tRNA von der P-Bindungsstelle freigesetzt.
Interessanterweise üben IF-2 und EF-TU analoge Funktionen aus: IF-2 erkennt nur Met-tRNAf, während EF-TU alle anderen Aminoacyl-tRNAs erkennt; beide Faktoren dienen dazu, eine Aminoacyl-tRNA an einer spezifischen Stelle auf dem Ribosom einzuführen. Darüber hinaus weisen die beiden Proteine über eine Länge von 100 Aminosäuren eine Homologie auf. Die Hydrolyse von GTP, das an EF-TU bzw. IF-2 gebunden ist, liefert an sich keine Energie für die Bindung der Aminoacyl-tRNA an das Ribosom. Die GTP-Hydrolyse stellt jedoch Energie für die Abspaltung des fest gebundenen EF-TU bzw. IF-2 vom Ribosom zu Verfügung. Die Energie für die Bildung der Peptidbindung wird auf der Stufe der Aminosäurebeladung der tRNA investiert. In diesem Zusammenhang werden zur Bildung der Esterbindung zwischen der Aminosäure und der 2'- oder 3'-OH-Gruppe der tRNA zwei Phosphatbindungen von ATP hydrolysiert. Alle anderen ATP- und GTP-Moleküle, die im Verlauf der P. hydrolysiert werden, dienen dazu, die Genauigkeit des Prozesses zu erhöhen.
4) Termination (Abschlussphase). Mit dem Auftreten eines Terminationscodons an der A-Bindungsstelle ist das Signal für die Beendigung des Syntheseprozesses gegeben. Man kennt drei prokaryontische Terminationsfaktoren: RF-1 ist spezifisch für die Terminationscodons UAA und UAG, während RF-2 spezifisch für UAA und UGA ist. RF-3 stimuliert RF-1 und RF-2, erkennt selbst jedoch keine Terminationscodons. RF-3 besitzt außerdem GTPase-Aktivität; wahrscheinlich beschleunigt dieser Faktor die Termination unter GTP-Verbrauch. Man kennt nur einen eukaryontischen Terminationsfaktor, der auch GTPase-Aktivität besitzt. Wahrscheinlich tritt der eIF-3 mit dem Ribosom in Wechselwirkung, wenn dieses die mRNA verlässt, und bewirkt eine Trennung der beiden Untereinheiten. Die vorausgehende Darstellung beschreibt die P. für ein Ribosom, es darf jedoch nicht außer Acht gelassen werden, dass das funktionale System das Polysom ist. Zu jeder Zeit sind mehrere Ribosomen entlang der mRNA angeordnet; die Ribosomen, die dem 3'-Ende am nächsten sind, tragen die längsten neu synthetisierten Polypeptidketten, während jene am 5'-Ende weniger Codons translatiert haben und deshalb ein kürzeres Peptid tragen. Initiation, Elongation (in verschiedenen Stadien) und Termination laufen also simultan auf derselben mRNA ab.
Die gebildeten Proteine erhalten ihre Tertiärstruktur bereits während des Syntheseprozesses. In vielen Fällen unterliegen sie einer nachträglichen Prozessierung, wodurch die Moleküle in die biologisch aktive Form überführt werden, z.B. durch Anlagerung bestimmter Gruppen oder durch Abspaltung bestimmter Aminosäuresequenzen (Posttranslationsmodifizierung). Bei der Biosynthese von Sekretproteinen sorgt entsprechend der Signalhypothese eine N-terminal synthetisierte Peptidsequenz für die Anlagerung des Ribosoms an die Membran des rauen endoplasmatischen Reticulums (ER), wodurch das Protein noch während der Synthese durch die Membran in das Innere der Kanälchen des ER geschleust wird, um dann nach außen zu gelangen.
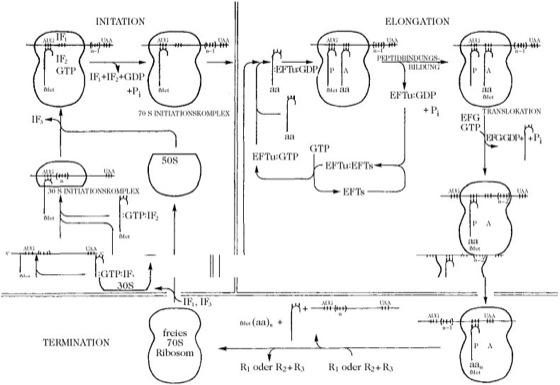
Proteinbiosynthese.Graphische Darstellung der Translation an prokaryontischen Ribosomen. Der Elongationszyklus beginnt durch die Wechselwirkung des 70S-Initiationskomplexes mit fMet-tRNA:EF-TU:GTP. In allen nachfolgenden Durchläufen des Zyklus tritt fMet-tRNA:EF-TU:GTP mit dem mRNA:Ribosom-Komplex, der die wachsende Polypeptidkette trägt, in Wechselwirkung. Die Termination setzt ein, wenn n Aminosäuren eingebaut wurden, wobei n der Anzahl an Codons zwischen dem Initiationscodon AUG und dem Terminationscodon (in diesem Beispiel UAA) entspricht.
Proteinbiosynthese. Tab. Prokaryontische und eukaryontische Synthesefaktoren.
| |||
| IF-1 | Gleichgewicht der Untereinheiten: 70S 50S + 30S Stabilisierung des Initiationskomplexes | ||
| IF-2 | Bindung von fMet-tRNAf an die 40S-Untereinheit; mRNA ist für diesen Vorgang nicht unbedingt notwendig | ||
| IF-3 | verhindert die Assoziation der 30S- und 50S-Untereinheiten | ||
| eIF-1 | 15 | Stabilisierung des Initiationskomplexes. | |
| eIF-2 | α-Untereinheit: 32-38; β-Untereinheit: 47-52; γ-Untereinheit: 50-54 | Bindung von Met-tRNA an die 40S-Untereinheit; der Vorgang benötigt GTP und läuft ab, bevor die mRNA gebunden wird | |
| eIF-2A | 50-96 | Bindung von Met-tRNAf an die 40S-Untereinheit; der Vorgang benötigt mRNA, jedoch kein GTP | |
| eIF-3 | 500-750 (Komplex aus 7-11 Polypeptiden) | verhindert die Assoziation der Ribosomenuntereinheiten; stabilisiert den Initiationskomplex | |
| eIF-4A | 48-53 | Bindung der mRNA an den 40S-Initiationskomplex | |
| eIF-4B | 80-82 | Bindung der mRNA an den 40S-Initiationskomplex | |
| eIF-4C | 19 | Stabilisierung des Initiationskomplexes | |
| eIF-4D | 17 | Stabilisierung des Initiationskomplexes | |
| eIF-5 | 125-160 | Abspaltung von eIF-2 und eIF-3 vom Initiationskomplex; Bindung der 60S-Untereinheit an den 40S-Komplex | |
| Cap-Erken- nungsprotein | 24 | bindet an mRNA-Cap | |
| EF-TU | 43 | GTP-EF-Tu bindet Aminoacyl-tRNA an ribosomale A-Bindungsstelle | |
| EF-TS | 35 | verdrängt GDP von EF-TU-GDP, das vom Ribosom abgespalten wurde; EF-TU:EF-TS-Komplex reagiert mit GTP unter Bildung von EF-TU-GTP | |
| EF-G | 80 | an der Translokation der Peptidyl-tRNA von der A- zur P-Bindungsstelle beteiligt; GTPase | |
| eEF-TU (EF-1α) | 53 | GTP-EF-Tu bindet Aminoacyl-tRNA an ribosomale A-Bindungsstelle | |
| eEF-TS (EF-1β) | 30 | verdrängt GDP von eEF-TU-GDP, das vom Ribosom abgespalten wurde; eEF-TU:eEF-TS-Komplex reagiert mit GTP unter Bildung von eEF-TU-GTP | |
| eEF-G (EF-2) | an der Translokation der Peptidyl-tRNA von der A- zur P-Bindungsstelle beteiligt | ||
| RF-1 | 47 | erkennt UAA- und UAG-Terminationscodons; spaltet Peptid von ribosomengebundener tRNA ab | |
| RF-2 | 35-48 | erkennt UAA- und UGA-Terminationscodons; spaltet Peptid von ribosomengebundener tRNA ab | |
| RF-3 | 46 | regt RF-1- und RF-2-Aktivitäten an | |
| eRF-3 | 56-105 | erkennt alle drei Terminationscodons; besitzt ribosomenabhängige GTPase-Aktivität |
Wenn Sie inhaltliche Anmerkungen zu diesem Artikel haben, können Sie die Redaktion per E-Mail informieren. Wir lesen Ihre Zuschrift, bitten jedoch um Verständnis, dass wir nicht jede beantworten können.